18072009 chemoinformatics bioinformatics
コマンドラインでタンパク質のポケットを探索してくれる。
論文によるとVoronoi tesselationをつかってalpha sphere detectionをやるみたい。
1R39に対して試してみた。
実行は
fpocket -f 1R39.pdb
と叩けば、ディレクトリが出来てPyMol,VMD用のファイルが出力される。
18072009 chemoinformatics bioinformatics
17072009 work
パターンランゲージとWikiの関係
無名の質とか
タオイズムっぽくつながるのも楽しい。
一方で、そういう質は捉えようとしても捉えられないものなのかなとも思った。
16072009 work
いつも社内競争倍率が高くて他の人に取られてしまうユーザー会に演者として呼んでもらえたので、5年ぶりくらいに参加できた。
いろいろと新しいヒトに逢えたりとか、会社を移って何年か会ってない人とか、学部の先輩にあったりとか、たまには違うユーザー会に出てみるのもいいものだなと思ったのであった。
で、僕のプレゼンが終わってから、先輩だったヒトに、プレゼンが僕らしいといわれたのだけど、どこが僕らしいのかは自分ではわからないもんですな。
いろいろと楽しい一日だった。
繰り返し経口投与
省略
CL = (F * (Dose/t)) / Cp,ss 10mgのデータからFを決定する
CLb=CLp/RbからRbをつかって全血基準のクリアランスを求める
t1/2をもとめる
一般に、薬物を持続投与する場合、消失半減期の5倍の時間が経っている時には定常状態に達しているとみてよいので これをもって定常状態の判断に利用してよい
> data <- read.csv("/Users/kzfm/PK/pk3-2.csv")
> data
dose cpss fe
A 10 0.000424 0.63
B 30 0.001350 0.66
C 100 0.004800 0.71
D 300 0.015700 0.77
E 500 0.027500 0.81
> attach(data)
> fp <- 0.5
> Rb <- 0.7
> Vd <- 30
> ka <- 1.5
> CLb <- (dose/12)/(cpss*1000*Rb)
> CLb
[1] 2.807727 2.645503 2.480159 2.274795 2.164502
> CLr <- CLb*fe
> CLr
[1] 1.768868 1.746032 1.760913 1.751592 1.753247
> CLh <- CLb - CLr
> CLh
[1] 1.0388589 0.8994709 0.7192460 0.5232029 0.4112554
最近、Journal of Pharmaceutical SciencesみたいなDMPKな雑誌を読むようになってきた。その中でScipyとpymcっていうpythonでMCMCができるモジュールを使って解析してた論文を見たので試したくなった。
sudo easy_install-2.6 pymc
でさくっと入って、テストしてみたらなんか色々こけてるようなのだけど、とりあえずサンプル写経
import pymc
import numpy as np
n = 5*np.ones(4,dtype=int)
x = np.array([-.86,-.3,-.05,.73])
alpha = pymc.Normal('alpha',mu=0,tau=.01)
beta = pymc.Normal('beta',mu=0,tau=.01)
@pymc.deterministic
def theta(a=alpha, b=beta):
"""theta = logit^{-1}(a+b)"""
return pymc.invlogit(a+b*x)
d = pymc.Binomial('d', n=n, p=theta,value=np.array([0.,1.,3.,5.]),observed=True)
これをmymodel.pyって名前で保存しておいて
対話環境から
>>> import mymodel
>>> import pymc
>>> S = pymc.MCMC(mymodel, db='pickle')
>>> S.sample(iter=10000, burn=5000, thin=2)
>>> pymc.Matplot.plot(S)
>>> pymc.Matplot.savefig("test.png")
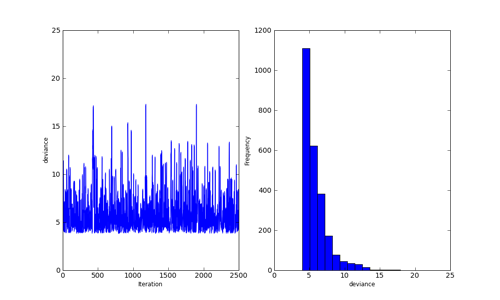
うーんMCMCわからん。精進せねば。
14072009 life
先日、はじめての現代数学を読んだとき、ゲーデルの不完全性定理がいまいちつかめんとか書いてた。
で、数学ガールの三作目がまさにゲーデルの不完全性定理をあつかったものらしく、今から楽しみ。
12072009 music drum'n'bass
設問1はクリアランスのパラメータを求める
設問2,3はi.v., p.o.それぞれの状況でパラメータを変えた場合どう変化するかを推定する
> data <- read.csv("/Users/kzfm/PK/pk31.csv")
> data
CLtot Vd fe fb Ka
A 0.2 0.1 1.00 0.1 1.5
B 0.2 10.0 1.00 0.1 1.5
C 1.3 0.1 0.02 0.1 1.5
D 1.3 10.0 0.02 0.1 1.5
> Qh <- 1.4
> Qr <- 1.1
> GFR <- 0.17
> Vb <- 0.077
> CLh <- (1-fe)*CLtot
> CLh
[1] 0.000 0.000 1.274 1.274
> CLr <- fe*CLtot
> CLr
[1] 0.200 0.200 0.026 0.026
> CLh_uint <- Qh*CLh/(fb*(Qh-CLh))
> CLh_uint
[1] 0.0000 0.0000 141.5556 141.5556
> CLr_uint <- Qr*(CLr -fb*GFR)/((Qr-CLr+fb*GFR)*fb)
> CLr_uint
[1] 2.19520174 2.19520174 0.09074244 0.09074244
AUCiv = D/CLtot
flip-flopを考える
富士の大山
冷やし大担麺。氷も入ってよく冷えとる。胡麻の風味がなかなかだが、思ったより辛くなかった。半ライスがついてて、残ったスープで食べるとうまいとのこと。

えびつけ麺(大盛り)
